10Xgenomic单细胞数据分析流程整理,虽然官网已经很详细,但是还是备份下
一、bcl2转fastq
安装 bcl2fastq,cellranger
下载bcl2fastq https://support.illumina.com/sequencing/sequencing_software/bcl2fastq-conversion-software/documentation.html
解压:
1 | unzip bcl2fastq2-v2-20-0-linux-x86-64.zip |
mkfastq 转格式:
1 | cellranger mkfastq --id=tiny-bcl2(结果目录命名) --run=/disk/zhw/zuo/10xGenomic/cellRanger/example/cellranger-tiny-bcl-1.2.0(解压目录) --csv=cellranger-tiny-bcl-simple-1.2.0.csv (输入文件) |
cellranger-tiny-bcl-simple-1.2.0.csv:
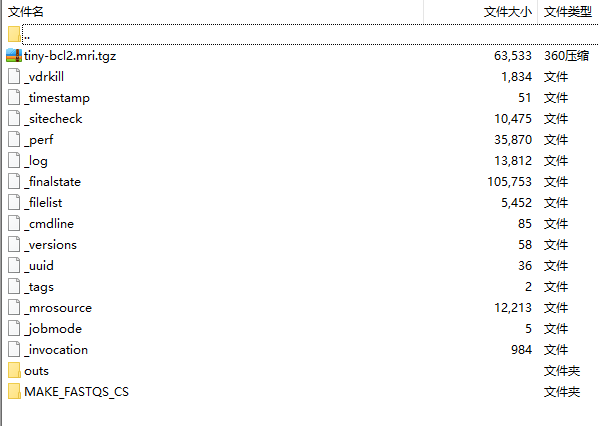
结果目录:tiny-bcl2:
cellranger-tiny-bcl-simple-1.2.0.csv:
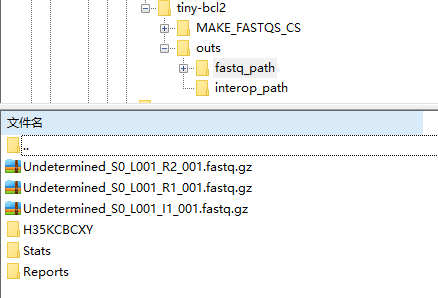
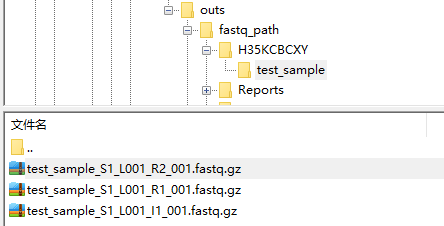
fastq结果:
二、fastq分析
1 | /disk/soft/cellranger-2.1.0/cellranger count --id=sample34(结果文件夹命名) --transcriptome=/disk/database/10xgenomic/refdata-cellranger-GRCh38-1.2.0(referent文件夹目录) --fastqs=/disk/zhw/zuo/10xGenomic/cellRanger/example/tiny-bcl2/outs/fastq_path(fastq文件目录) --sample=test_sample(可选,指定哪些样本的前缀) --expect-cells=1000 (期望回收细胞数量) |
–chemistry threeprime ()
1 | cellranger count --id=SC-3_mm10 --localcores=20 --transcriptome=/disk/database/10xgenomic/refdata-cellranger-mm10-1.2.0 --fastqs=/disk/zhw/zhou/Zhou_10XGenomic_1801/0-FASTQ/SC-3 --chemistry threeprime |
1 | cellranger count --id=neurons --localcores 5 --transcriptome=/disk/database/10xgenomic/refdata-cellranger-mm10-1.2.0 --fastqs=/disk/zhw/zhou/Zhou_10XGenomic_1801/test --expect-cells=900 |
1 | /disk/soft/cellranger-2.1.0/cellranger count --id=SC-3-count --transcriptome=/disk/database/10xgenomic/refdata-cellranger-GRCh38-1.2.0 --fastqs=/disk/zhw/zhou/Zhou_10XGenomic_1801/0-FASTQ/SC-3 --sample=SC-3(fastq前缀) |
–sample:
cellranger-tiny-bcl-simple-1.2.0.csv:
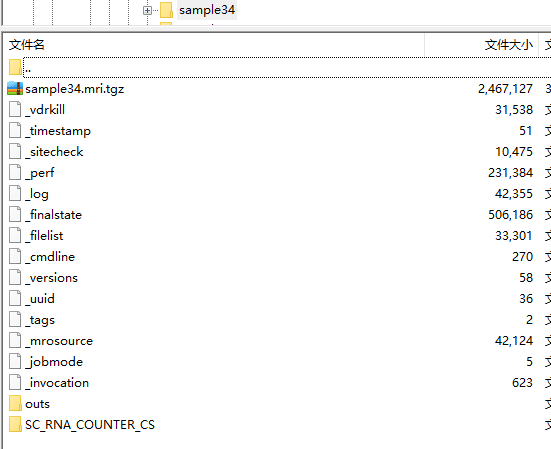
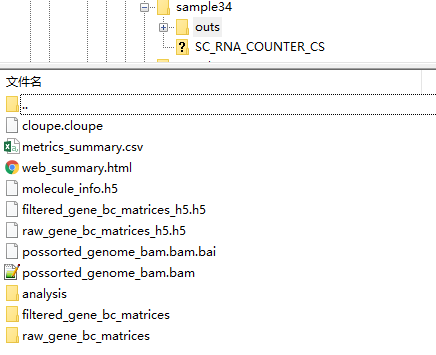
sample34/outs,web_summary.html为网页结果。
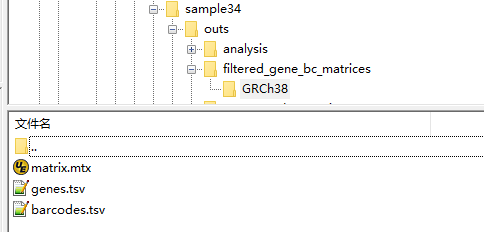
filtered_gene_bc_matrices为稀疏矩阵,转可以为普通矩阵
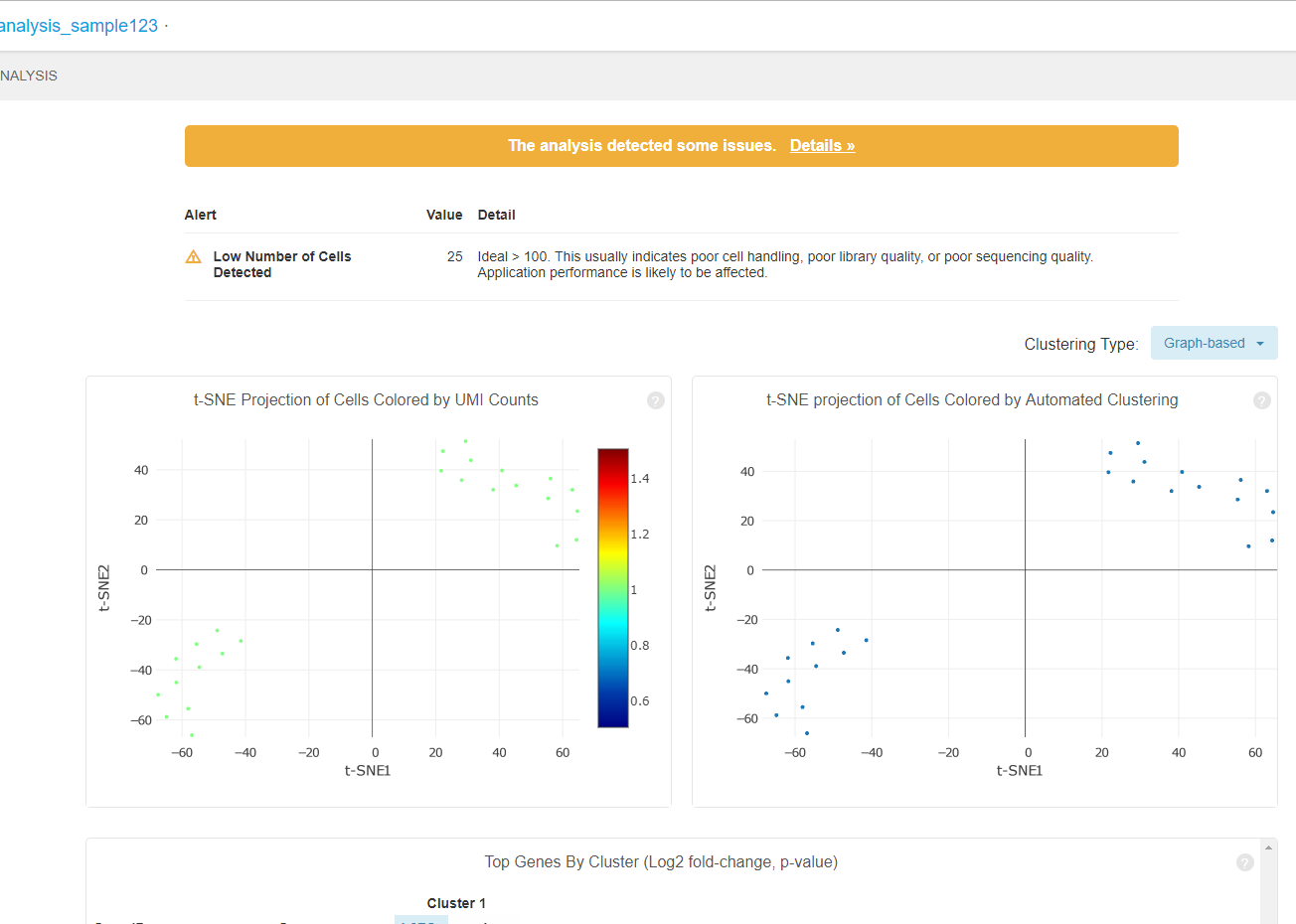
三、 再分析reanalyze
1 | cellranger reanalyze --id=SC-4 --matrix=/disk/zhw/zhou/Zhou_10XGenomic_1801/2_cellranger_count/SC-4-count-mm10/outs/filtered_gene_bc_matrices_h5.h5 |
四、 cellrangerRkit R包第二步分析
稀疏矩阵转为密集矩阵:
1 | pbmc.data_SC4 <- Read10X(data.dir = "/disk/zhw/zhou/Zhou_10XGenomic_1801/1-MAPPING/sample_SC-4/outs/filtered_gene_bc_matrices/mm10") |
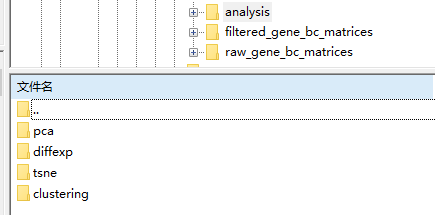
第一步cellranger mkfastq分析之后第二步分析,主要是tsne,PCA,k-means聚类,差异表达分析和热图
cellrangerRkit
五、R包Seurat分析
参考生信技能树的这篇文章:
六、建reference
如果不想用官方的ref,可以自己建立
需要提供fa文件和gtf文件
不可以直接改
需要用cellrager
单个物种:
1 | cellranger mkref --nthreads=40 --genome=ref-mm10-hg38-HBB2 --fasta=/disk/database/10xgenomic/mm10-hg38-HBB-data/fasta/genome_mm10_humanHBB.fa --genes=/disk/database/10xgenomic/mm10-hg38-HBB-data/genes/gene.gtf |
两个物种:
1 | cellranger mkref --genome=hg38 --fasta=/disk/database/mouse/UCSC-mm10/mm10.fa --genes=/disk/database/mouse/gencode.vM10.annotation.gtf --genome=mm10 --fasta=/disk/database/human/hg38/Gencode/genome.fa --genes=/disk/database/human/hg38/Gencode/gencode.v25.annotation.gtf |